通常我们做完荧光定量PCR后,会通过下机数据来分析基因表达情况。这篇干货将会给大家详细分享荧光定量PCR数据处理方法,希望能给小伙伴们一定的帮助。
相对定量法中常见的是比较Ct法,其中主要包括△△Ct法,Pfaffl法和△CT法,目前诸多科研人员采用最多的是△△Ct法。虽然该方法应用广泛,但是很多人却不了解其中的原理。知其然,知其所以然。小翌接下来给小伙伴们讲一下△△Ct法的原理。
△△Ct法原理
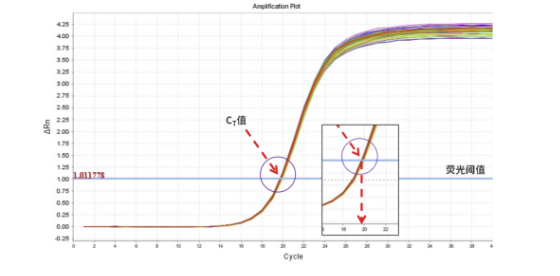
Ct值:每个反应管中荧光信号达到设定的荧光阈值时所需要的循环数。起始模板拷贝数越多, Ct值则越小。
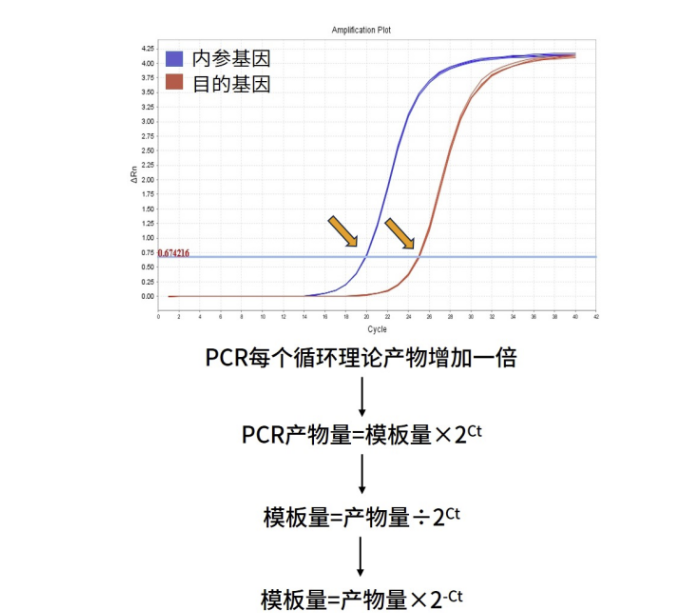
理论条件下,DNA扩增是以半保留复制的形式每个循环增加一倍,由100条变200条,由200条变400条,由400条变800条等等,用数学表达式来说就是2^Ct。但是实际情况中,扩增效率不是100%的,增量的表达形式则变成了(1+e)^Ct,其中e表示的是扩增效率。
扩增产量=起始模板量×(1+e)^Ct
由于不同反应条件下,e值不一样,为便捷地计算,分析数据时将e默认为100%,那么扩增产量=起始模板量×2^Ct。
看到这,有小伙伴可能会想,在一样的产物量(荧光信号水平)下,比较Ct值,那我就可以比较不同实验组的起始模板量,是不是就可以得出基因表达差异的结果了。然而事实并非如此,不同实验组难以保证上样量的一致性、生物本身的一致性、整体操作误差的一致性,做出来的结果是有偏差的,甚至可能是相反的。这里给小伙伴们举个例子。
药物测试实验案例
测试一款减少黑色素表达的药物,该药物以灌胃的形式给药至实验组小鼠,对照组小鼠仅以正常饮用水进行灌胃,以往大量研究已表明该药物对于黑色素表达有明显的抑制作用。
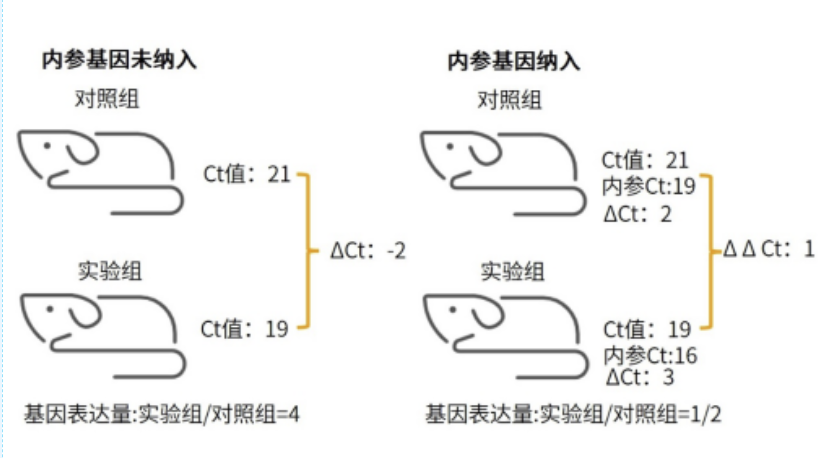
如果研究目的基因,简单仅以两组的目的基因表达量相比,可以发现,实验组生成黑色素的基因表达量相比于对照组要多四倍。
然而已有大量研究证明该药物抑制黑色素表达,计算结果与已有理论存在相悖的情况(也有可能是发现了新课题o(* ̄▽ ̄*)ブ)。为什么会出现这个结果呢?其原因可能主要是两组小鼠RNA提取的时候处于不同的时间、提取样本量不一样、cDNA上样量不一样、cDNA浓度不一样等等。
为避免各类潜在差异带来的影响,需引入内参基因,可见上图右半部分。内参基因通常是一种始终保持着低水平甲基化且一致处于活性转录状态的基因,高度保守且在大多数情况下持续表达,其表达水平受环境因素影响较小。通常在检测基因的表达水平时用作参照物,可用以校正操作、上样量差异等带来的实验误差,从而保证结果的准确性。
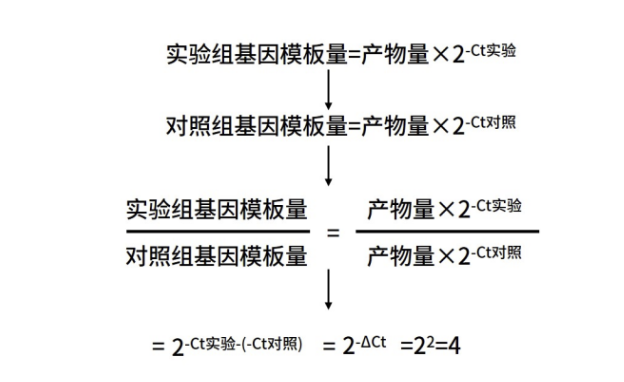
同样样本,在原测试目的基因的基础上,加测内参基因。对照组得到的目的基因与内参基因之间的模板比值为正常老鼠目的基因的比例关系,理论状态下,以该比例×实验组老鼠恒定表达的内参基因表达量即可获得实验组老鼠在正常状态下目的基因的理论表达量,实际实验组老鼠目的基因表达量除以理论表达值,即可计算出老鼠在药物处理下,目的基因的表达量变化情况,具体如下:
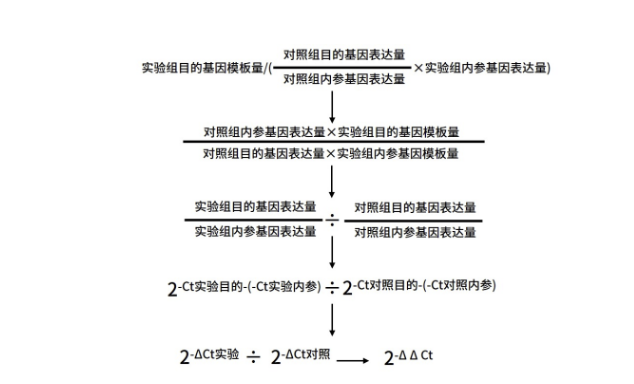
以上结果可以得出,实验组目的基因表达量仅为对照组的1/2,也符合以往研究报道。
是不是小伙伴们以为△△Ct法原理的描述到这里就结束了?不不不,我们上文中有提到实际情况中扩增产量=起始模板量×(1+e)^Ct,为便捷计算,分析数据时将扩增效率e默认为100%,那么扩增产量=起始模板量×2^Ct。我们在实际做实验的时候,也要注意内参基因和目的基因所对应的扩增效率控制在接近100%或者基本一致,否则△△Ct法得出的结果和实际情况会有出入。
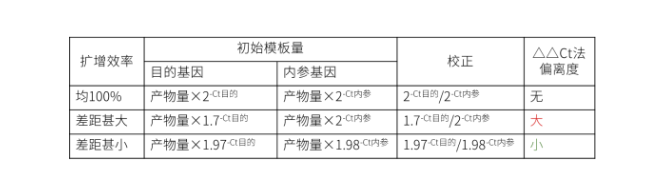
如上表格,若内参基因和目的基因扩增效率上未控制在基本一致或接近100%,则在使用△△Ct法上会有一定的偏差风险。
数据处理案例解析
假设目前需要研究甲药物对小鼠X基因表达的影响,以未经过任何处理的小鼠作为对照组,实验组为经过不同量药物处理过的小鼠,分别提取RNA进行反转录,以得到的cDNA为模板,选择小鼠GAPDH基因作为内参,进行qPCR实验。
上机设置的qPCR孔如下
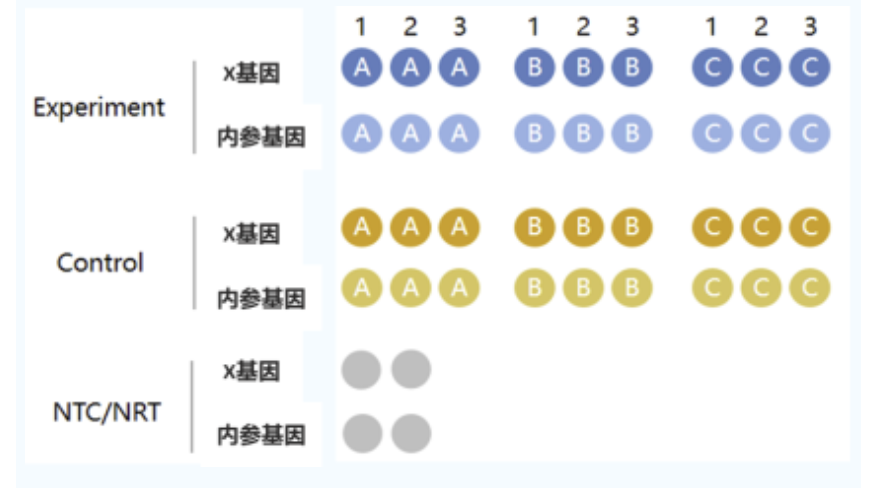
图示说明:
1)NTC:以水代替模板,用来验证PCR体系中是否存在污染,每一对引物都需要做NTC;
2)NRC:是指用未经反转录的RNA作为模板,是对gDNA残留的控制,每一个样本都需要做NRC;
3)生物学重复:不同的样本(ABC);
4)技术重复:实际上就是同一材料包括的复孔(123)。
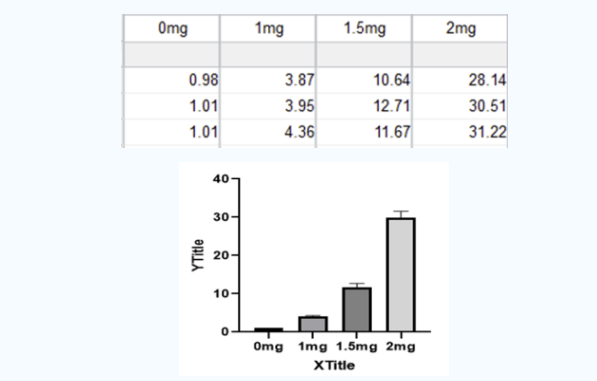
下机处理的Excel数据如下
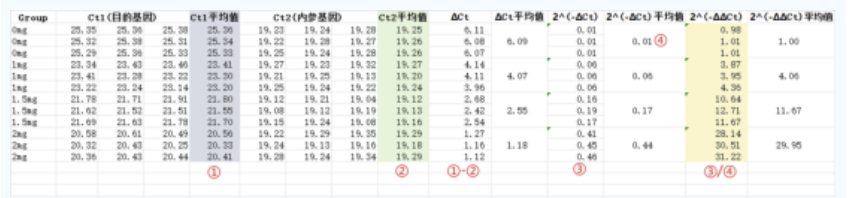
图示说明:
1)0mg:未经过任何处理的小鼠-对照组;
2)④:对照组校正后的数值;
3)③/④:每个小组校正后的数值比上对照组校正后的数值;
4)注意图表上的数据在excel中采用了保留2位小数的形式,实际计算时不可忽略小数点后的所有数字,减少按数字的动作,活用Excel。
GraphPad中进行绘图分析
种草推荐
目前翌圣qPCR mix系列的产品已经荣登Nature、 Cell等多个顶级期刊,获得科研大牛们认可!以下仅展示部分助力发表的高分文章:
[1] Li Y, Wang D, Ping X, et al. Local hyperthermia therapy induces browning of white fat and treats obesity. Cell. 2022;185(6):949-966.e19.doi:10.1016/j.cell.2022.02.004.(IF=66.850)
[2] Seki T, Yang Y, Sun X, et al. Brown-fat-mediated tumour suppression by cold-altered global metabolism. Nature. 2022;608(7922):421-428. doi:10.1038/s41586-022-05030-3. (IF=69.504)
[3] Chen P, Wang W, Liu R, et al. Olfactory sensory experience regulates gliomagenesis via neuronal IGF1. Nature. 2022;606(7914):550-556. doi:10.1038/s41586-022-04719-9.(IF=69.504)
[4] Dong W, Zhu Y, Chang H, et al. An SHR-SCR module specifies legume cortical cell fate to enable nodulation. Nature. 2021;589(7843):586-590. doi:10.1038/s41586-020-3016-z.(IF=69.504)
[5] Lu XY, Shi XJ, Hu A, et al. Feeding induces cholesterol biosynthesis via the mTORC1-USP20-HMGCR axis. Nature. 2020;588(7838):479-484. doi:10.1038/s41586-020-2928-y.(IF=69.504)
[6] Bi X, Wang K, Yang L, et al. Tracing the genetic footprints of vertebrate landing in non-teleost ray-finned fishes. Cell. 2021;184(5):1377-1391.e14. doi:10.1016/j.cell.2021.01.046.(IF=66.850)
[7] Liu S, Hua Y, Wang J, et al. RNA polymerase III is required for the repair of DNA double-strand breaks by homologous recombination. Cell. 2021;184(5):1314-1329.e10. doi:10.1016/j.cell.2021.01.048.(IF=66.850)
[8] Liu CX, Li X, Nan F, et al. Structure and Degradation of Circular RNAs Regulate PKR Activation in Innate Immunity. Cell. 2019;177(4):865-880.e21. doi:10.1016/j.cell.2019.03.046.(IF=66.850)
[9] Han X, Wang R, Zhou Y, et al. Mapping the Mouse Cell Atlas by Microwell-Seq. Cell. 2018;172(5):1091-1107.e17. doi:10.1016/j.cell.2018.02.001.(IF=66.850)
[10] Chai Q, Yu S, Zhong Y, et al. A bacterial phospholipid phosphatase inhibits host pyroptosis by hijacking ubiquitin. Science. 2022;378(6616):eabq0132. doi:10.1126/science.abq0132.(IF=63.714)
[11] Yu Q, Liu S, Yu L, et al. RNA demethylation increases the yield and biomass of rice and potato plants in field trials. Nat Biotechnol. 2021;39(12):1581-1588. doi:10.1038/s41587-021-00982-9.(IF=68.164)
[12] Han F, Liu X, Chen C, et al. Hypercholesterolemia risk-associated GPR146 is an orphan G-protein coupled receptor that regulates blood cholesterol levels in humans and mice. Cell Res. 2020;30(4):363-365. doi:10.1038/s41422-020-0303-z.(IF=46.297)
[13] Wang Z, Lu Z, Lin S, et al. Leucine-tRNA-synthase-2-expressing B cells contribute to colorectal cancer immunoevasion. Immunity. 2022;55(6):1067-1081.e8. doi:10.1016/j.immuni.2022.04.017.(IF=43.474)
[14] Bi Q, Wang C, Cheng G, et al. Microglia-derived PDGFB promotes neuronal potassium currents to suppress basal sympathetic tonicity and limit hypertension. Immunity. 2022;55(8):1466-1482.e9. doi:10.1016/j.immuni.2022.06.018.(IF=43.474)
[15] Wang X, Ni L, Wan S, et al. Febrile Temperature Critically Controls the Differentiation and Pathogenicity of T Helper 17 Cells. Immunity. 2020;52(2):328-341.e5. doi:10.1016/j.immuni.2020.01.006.(IF=43.474)
[16] Xiao J, Li W, Zheng X, et al. Targeting 7-Dehydrocholesterol Reductase Integrates Cholesterol Metabolism and IRF3 Activation to Eliminate Infection. Immunity. 2020;52(1):109-122.e6. doi:10.1016/j.immuni.2019.11.015.(IF=43.474)
[17] Zhang X, Zhang C, Qiao M, et al. Depletion of BATF in CAR-T cells enhances antitumor activity by inducing resistance against exhaustion and formation of central memory cells. Cancer Cell. 2022;40(11):1407-1422.e7. doi:10.1016/j.ccell.2022.09.013.(IF=38.585)
[18] Wang XY, Wei Y, Hu B, et al. c-Myc-driven glycolysis polarizes functional regulatory B cells that trigger pathogenic inflammatory responses. Signal Transduct Target Ther. 2022;7(1):105. Published 2022 Apr 18. doi:10.1038/s41392-022-00948-6.(IF=38.104)
[19] Fan H, Hong B, Luo Y, et al. The effect of whey protein on viral infection and replication of SARS-CoV-2 and pangolin coronavirus in vitro. Signal Transduct Target Ther. 2020;5(1):275. Published 2020 Nov 24. doi:10.1038/s41392-020-00408-z.(IF=38.104)
[20] Ren Y, Wang A, Wu D, et al. Dual inhibition of innate immunity and apoptosis by human cytomegalovirus protein UL37x1 enables efficient virus replication. Nat Microbiol. 2022;7(7):1041-1053. doi:10.1038/s41564-022-01136-6.(IF=30.964)
<上下滑动查看更多>
翌圣生物基因研究完整解决方案
产品特别推荐
|
方法 |
分类 |
产品名称 |
货号 |
|
RNA提取 |
同Trizol提取 |
TRIeasy™ Total RNA Extraction Reagent |
|
|
免氯仿升级版 |
TRIeasy™ Total RNA Extraction Reagent(Tcm Free) |
||
|
动物组织/细胞总RNA提取,避开有毒试剂,最快15 min完成 |
MolPure® Cell/Tissue Total RNA Kit细胞/组织总RNA提取试剂盒 |
||
|
反转录试剂 |
5 min一步gDNA去除&反转录预混液(下游应用qPCR) |
Hifair® AdvanceFast One-step RT-gDNA Digestion SuperMix for qPCR |
|
|
5 min快速反转,最长可满足14 kb cDNA合成,含gDNA去除(下游应用PCR/qPCR) |
Hifair® AdvanceFast 1st Strand cDNA Synthesis Kit |
11149/11150ES |
|
|
高质量第一链cDNA合成预混液,含gDNA去除(下游应用qPCR) |
Hifair® III 1st Strand cDNA Synthesis SuperMix for qPCR (gDNA digester plus) |
||
|
qPCR染料法 |
高特异高荧光值定量预混液(染料法) |
Hieff UNICON® Advanced qPCR SYBR Master Mix |
|
|
高灵敏通用型定量预混液(染料法) |
Hieff UNICON® Universal Blue qPCR SYBR Master Mix |
||
|
超高性价比定量预混液 (染料法),已发文章累计IF达到5000+ |
Hieff® qPCR SYBR Green Master Mix (No Rox) |
||
|
Hieff® qPCR SYBR Green Master Mix (Low Rox) |
|||
|
Hieff® qPCR SYBR Green Master Mix (High Rox) |
